Alicia Abadía Cardoso
Universidad Autónoma de Baja California, Facultad de Ciencias Marinas, Baja California, México
Es Profesora-Investigadora de Tiempo Completo en la Facultad de Ciencias Marinas de la Universidad Autónoma de Baja California (uabc) desde 2015. Es integrante del Sistema Nacional de Investigadoras e Investigadores nivel 1 y cuenta con el perfil prodep. Se formó como bióloga en la unam, estudió la maestría en Ecología Marina en cicese y el doctorado en Ciencias del Mar en la Universidad de California en Santa Cruz. Realizó una estancia postdoctoral en el laboratorio de Ecología Molecular y Análisis Genético de la noaa en los Estados Unidos. Su línea de investigación principal consiste en aplicar métodos novedosos de genética molecular y genómica para abordar cuestiones sobre ecología, evolución, conservación y manejo de especies acuáticas de importancia ecológica y económica, desde mamíferos marinos y peces hasta, recientemente, invertebrados. Se interesa en promover la conservación de la biodiversidad mediante la evaluación de la variabilidad genética de las poblaciones, los niveles de endogamia, las incertidumbres taxonómicas y el impacto de la presión pesquera, la fragmentación del hábitat y el cambio climático.
aabadia@uabc.edu.mx
ORCID: 0000-0003-0691-0358
Sitio: aabadia.com
Yolanda Schramm Urrutia
Universidad Autónoma de Baja California, Facultad de Ciencias Marinas, Baja California, México
Es profesora-investigadora en la uabc, en la Facultad de Ciencias Marinas, desde 1998. Actualmente ostenta el nombramiento de Profesora Ordinaria de Carrera Titular Nivel c. Es Bióloga por la Universidad Autónoma de Guadalajara (1993) y tiene Maestría y Doctorado en Ciencias en Oceanografía Costera por la uabc (1997 y 2002). Miembro del Sistema Nacional de Investigadoras e Investigadores desde 2007, con el nombramiento de nivel II. Imparte cursos en las licenciaturas en Oceanología, Ciencias Ambientales, Acuacultura y Biología, además de en el posgrado en Oceanografía Costera. Sus líneas de investigación son la Mastozoología Marina y la Ecología Molecular. Ha estudiado las cuatro especies de pinnípedos que habitan en México por más de 20 años, desarrollando principalmente proyectos en las islas y la costa al oeste de la península de Baja California. Sus proyectos de investigación se enfocan en la conservación y resolución de problemas en la región, utilizando diversas herramientas de campo y técnicas moleculares.
yschramm@uabc.edu.mx
ORCID: 0000-0001-6951-4884
Ivone Giffard Mena
Universidad Autónoma de Baja California, Facultad de Ciencias Marinas, Baja California, México
Obtuvo su título en Oceanología en 1995 en la Facultad de Ciencias Marinas de la uabc. Posteriormente, completó su Maestría en Ciencias en el cicese y su Doctorado en la Universidad de Montpellier 2, Francia, en 2004 y 2007, respectivamente. Actualmente, es Profesora-Investigadora Titular c y Coordinadora de Investigación y Posgrado en la Facultad de Ciencias Marinas de la uabc. Miembro del Sistema Nacional de Investigadoras e Investigadores nivel II y miembro regular de la Academia Mexicana de Ciencias. La Dra. Giffard Mena ha desarrollado una destacada carrera en biología molecular, ecofisiología de peces y crustáceos, y virología marina. Su investigación incluye el desarrollo de tratamientos antivirales para camarones, el estudio de la osmoregulación en especies marinas, y la aplicación de técnicas de secuenciación para estudiar mamíferos marinos y plantas costeras.
igiffard@uabc.edu.mx
ORCID: 0000-0003-1688-0703
Página en la FCM: fcm.ens.uabc.mx/~igiffard
Facebook: Yavo28
Arlette Pacheco Sandoval
Universidad Autónoma de Baja California, Facultad de Ciencias Marinas, Baja California, México
Es becaria posdoctoral en la uabc desde febrero de 2024. Obtuvo su licenciatura en Biología en la uabc y completó su maestría y doctorado en Ciencias de la Vida con orientación en Biología Ambiental en el cicese. Actualmente, es Candidata del Sistema Nacional de Investigadores (sni). Durante los últimos ocho años, ha sido pionera en el estudio de la microbiota intestinal de pinnípedos en México, enfocando su investigación en cómo diversos factores influyen en la composición microbiana de estos animales. Ha publicado cuatro artículos científicos en revistas indexadas. Su proyecto postdoctoral actual se centra en investigar la dinámica de la transmisión bacteriana, con énfasis en bacterias patógenas para pinnípedos y humanos, contribuyendo al desarrollo de políticas de conservación para mamíferos marinos en México.
pacheco.arlette06@gmail.com
ORCID: 0000-0003-0718-3391
Jennyfers Chong Robles
Universidad Autónoma de Baja California, Facultad de Ciencias Marinas, Baja California, México
Es bióloga marina por la Universidad del Mar, con maestría en Ecología Marina (cicese) y doctorado en Ecología Molecular y Biotecnología (uabc). Tiene una formación académica y profesional interdisciplinaria. Ha realizado dos estancias posdoctorales, una en secuenciación masiva (cicese) y otra en acuacultura (uabc). Ha adquirido amplia experiencia en biología molecular y en el uso de la secuenciación masiva en el instrumento MiSeq. Sus intereses de investigación se centran en la fisiología de invertebrados, combinando experimentos de laboratorio con técnicas de biología molecular y genómica. Actualmente, es profesora de asignatura en la uabc y en la Universidad Xochicalco, y ofrece servicios profesionales para el procesamiento de muestras de secuenciación masiva.
jennyfer.chong@gmail.com
ORCID: 0000-0001-8634-4354
Resumen
La totoaba, un pez único de México, estuvo al borde de la extinción debido a la sobrepesca. Para salvarla, la Universidad Autónoma de Baja California ha logrado avances significativos con un proyecto de reproducción en cautiverio. Pero aún falta mucho por aprender sobre su biología, como qué come en su hábitat natural. Afortunadamente, técnicas genéticas innovadoras, como la metagenómica, ahora nos permiten conocer con precisión las especies que forman parte de su dieta. Este descubrimiento no sólo mejora las estrategias de conservación de la totoaba en su entorno natural, sino que también optimiza su desarrollo en cautiverio. Al entender mejor sus necesidades alimenticias, se pueden tomar decisiones más informadas para proteger a esta especie en peligro y asegurar su futuro.
Palabras clave: totoaba, conservación, metagenómica, extinción, dieta.
What’s on the totoaba’s plate? Discover its diet with forensic science
Abstract
The totoaba, a unique fish from Mexico, was on the brink of extinction due to overfishing. To save it, the Autonomous University of Baja California has made significant progress with a captive breeding project. However, much is still to be learned about its biology, such as what it eats in its natural habitat. Fortunately, innovative genetic techniques, such as metagenomics, now allow us to accurately identify the species that make up its diet. This discovery not only enhances conservation strategies for the totoaba in its natural environment but also optimizes its development in captivity. By better understanding its nutritional needs, more informed decisions can be made to protect this endangered species and secure its future.
Keywords: totoaba, conservation, metagenomics, extinction, diet.
En el corazón del Golfo de California
El operativo de la Procuraduría Federal de Protección al Ambiente (profepa) fue un golpe certero: cuatro totoabas, dos hembras y dos machos de entre 81 y 136 cm, que por su tamaño eran consideradas adultas (Berdegué, 1955), fueron decomisadas. Estas fueron capturadas en una red de pesca ilegal y retiradas rápidamente de las aguas del Golfo de California, donde ya no tenían escape. Las “policías del mar” las sacaron del agua, frescas, y con un futuro incierto. Esta acción no sólo representó un acto de justicia en el océano, sino que también ofreció la oportunidad de desvelar uno de los secretos mejor guardados de estos gigantes marinos: ¿qué comen realmente las totoabas en su hábitat natural?
Las totoabas (Totoaba macdonaldi), esos imponentes gigantes marinos que habitan en el Golfo de California, han intrigado a los científicos durante décadas. ¿De qué se alimentan? ¿Cómo entendemos su dieta? A través de la ciencia y la genética, se ha logrado desvelar parte de sus secretos mediante el uso de técnicas innovadoras.
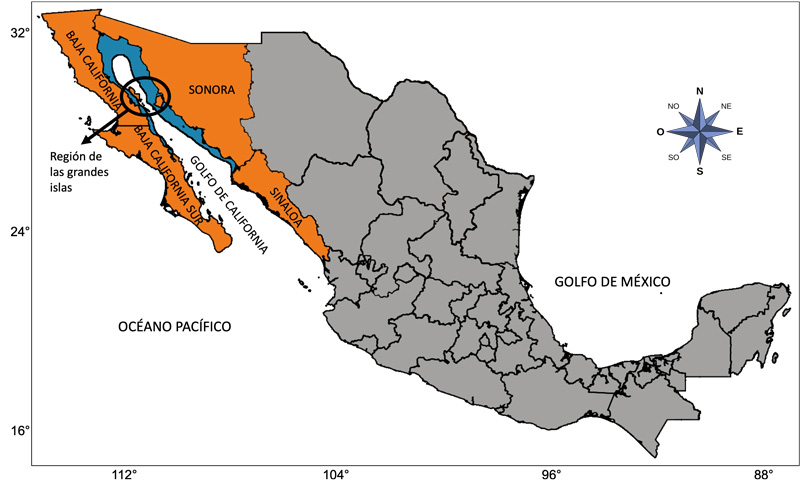
¡La totoaba es un pez realmente grande! Puede medir hasta dos metros y alcanzar un peso de 135 kg cuando es adulto. Este pez habita exclusivamente en las zonas costeras del Golfo de California, desde el Delta del Río Colorado, pasando por las costas de Baja California y Sonora, hasta llegar a Sinaloa (Figura 1) (Cisneros-Mata et al., 1995). Es tan única que sólo se encuentra en este ecosistema, lo que la convierte en una especie endémica. Además, las totoabas migran para reproducirse. Entre febrero y mayo, todas viajan hacia el Delta del Río Colorado, donde se agrupan. Después de este periodo, los juveniles y adultos regresan al sur, hacia las aguas más profundas de las grandes islas (Berdegué, 1955; Cisneros-Mata et al., 1995).
Figura 1. Distribución de la totoaba en la zona costera del Alto Golfo de California (en azul).
Crédito: modificado de Arvizu y Chávez, 1972.
Durante varias décadas, la pesca indiscriminada de totoaba casi llevó a la especie a la extinción. En 1975, la totoaba fue declarada en peligro de extinción, y se prohibió su pesca (semarnat, 2010). Sin embargo, a pesar de los esfuerzos por protegerla, la totoaba se asemeja a otro pez muy valorado en Asia, el bahaba, al que se le atribuyen, de manera infundada, propiedades medicinales y afrodisíacas. Este pez está tan amenazado debido a la sobrepesca que su captura ilegal comenzó a verse como una alternativa. Así nació el tráfico ilegal de totoaba, cuyo destino final era el mercado asiático (Cisneros-Mata et al., 2020).
¿Qué ocurre cuando una especie está al borde de la extinción?
Cuando una especie se encuentra en riesgo de desaparecer, se implementan estrategias para incrementar su población. En 1994, la Universidad Autónoma de Baja California (uabc) inició un ambicioso proyecto para recuperar la totoaba, una especie clave tanto ecológica como económicamente para la región. El proyecto se enfocó en su reproducción en cautiverio con tres objetivos principales:
- Estudiar la biología de la especie.
- Producir totoabas para el consumo humano y reducir la pesca de ejemplares silvestres.
- Liberar juveniles en el Alto Golfo de California para favorecer su recuperación.
Gracias a este esfuerzo y al trabajo conjunto con otras instituciones, se han liberado más de 500,000 juveniles en su hábitat natural (Enríquez Paredes et al., 2023). Además, desde 2011, la carne de totoaba cultivada en la uabc se comercializa de manera legal (Figura 2) (Enríquez Paredes et al., 2023).
Figura 2. Cultivo de totoabas en la Universidad Autónoma de Baja California (arriba). De izquierda a derecha: juvenil de totoaba, tanque con totoabas juveniles, totoabas adultas reproductoras.
Crédito: L. Enríquez, I. Giffard (2019).
No obstante, para mejorar el éxito de este proyecto es necesario profundizar en el conocimiento de la biología de la totoaba en su entorno natural. Comprender su dieta requiere estudiar su hábitat a lo largo de las distintas etapas de su vida (juveniles, preadultos y adultos), sus migraciones y sus necesidades energéticas. Esta información permite diseñar dietas óptimas en laboratorio para su crianza en cautiverio.
¿Cómo descubrimos lo que come la totoaba?
Investigar la dieta de una especie requiere el uso de diversas técnicas (Nielsen et al., 2018), y la elección de la más adecuada depende de los hábitos alimenticios de la especie en cuestión.
- Observación directa. Esta técnica es útil para especies terrestres, pero resulta inviable en el caso de la totoaba, que habita en el mar, lo que impide presenciar sus hábitos alimenticios en tiempo real.
- Análisis de excretas. Permite identificar restos de alimentos, pero para la totoaba, recolectar muestras resulta complicado debido a su entorno.
- Análisis de contenido estomacal. Implica capturar ejemplares y examinar sus estómagos en busca de restos de presas. Este método tradicional requería sacrificar múltiples individuos y dependía de que el alimento no estuviera completamente digerido.
Sin embargo, para las especies en peligro de extinción, la extracción de estómagos resulta inviable. Por ello, se ha recurrido a una técnica más avanzada: la metagenómica, que consiste en el estudio del adn presente en una muestra para identificar las especies que han interactuado con ella, incluso si ya han sido digeridas (Pompanon et al., 2012).
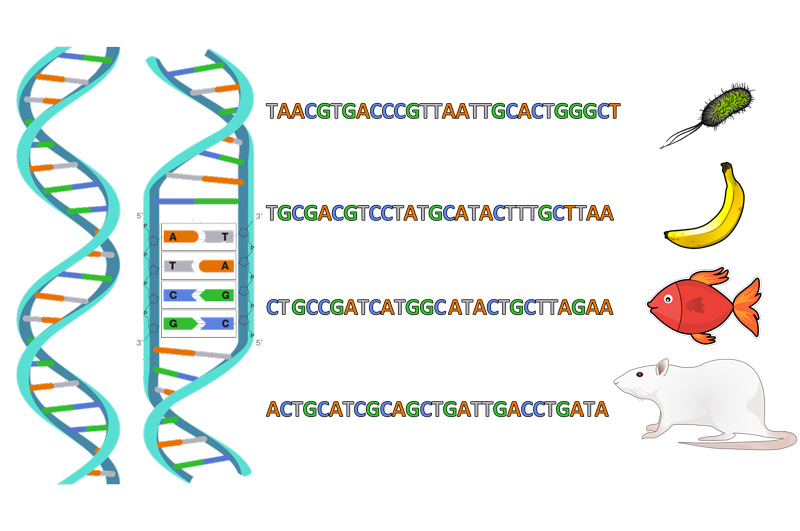
El adn, compuesto por cuatro nucleótidos1 (adenina [A], guanina [G], citosina [C] y timina [T]), forma secuencias únicas en cada especie (Figura 3) (Watson y Crick, 1953). Al analizar el contenido estomacal de una totoaba mediante metagenómica, se pueden identificar las especies consumidas con gran precisión (Fernandes et al., 2018).
Los nucleótidos son las unidades básicas que forman el adn.
Figura 3. Diagrama de la estructura de una molécula de ADN. Cada especie tiene una secuencia única de nucleótidos (letras), lo que permite su identificación a partir del ADN.
Crédito: A. Abadía (2023).
Análisis forense: descifrando la dieta de la totoaba
Tras el decomiso de las totoabas, surgió una nueva oportunidad para entender más a fondo a estos gigantes marinos. El análisis forense, utilizando la innovadora técnica metagenómica, permitió adentrarse en el misterio de su dieta. Al emplear esta técnica, los científicos pudieron descifrar los secretos de lo que las totoabas realmente consumen en su hábitat natural, incluso cuando los restos de su alimentación ya han sido digeridos.
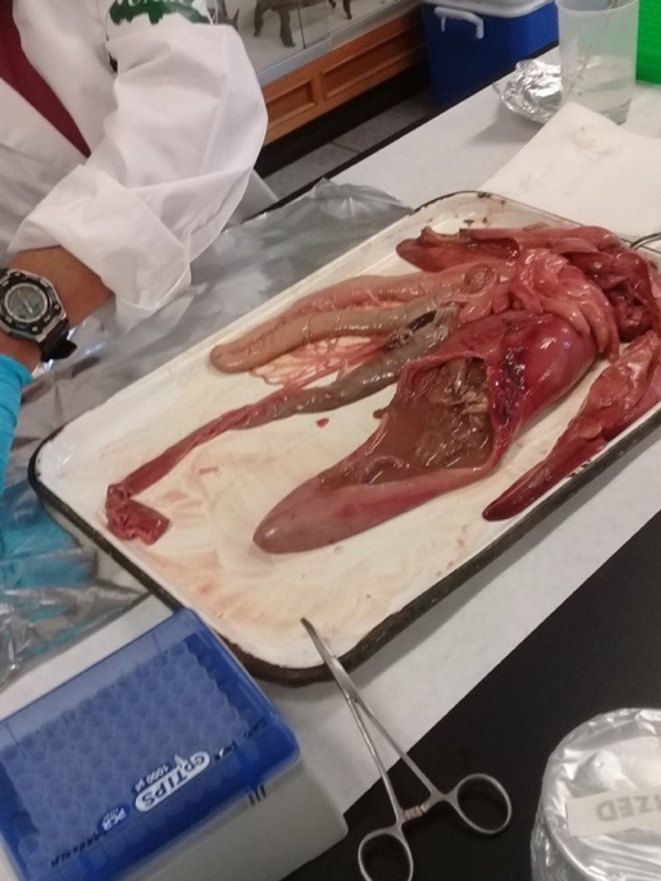
Figura 4. Estómago de totoaba abierto para la obtención de muestras (~0.02 g), las cuales se colocaron en tubos para la posterior extracción de ADN.
Crédito: A. Abadía (2020).
El proceso comenzó con una disección minuciosa de los ejemplares. Se realizó un corte continuo desde la base de la boca hasta el costado, para exponer los órganos sin moverlos de su lugar. Una vez identificados los órganos, se extrajeron para ser pesados y medidos.
Luego, se extrajo el adn de cada muestra y se secuenció, obteniendo las secuencias de nucleótidos únicas de cada especie presente en el contenido estomacal. Estas secuencias se compararon con las de una base de datos global llamada GenBank, que alberga información genética de miles de especies.
Este trabajo se llevó a cabo en colaboración con el grupo de Nutrición Acuícola de la uabc, quienes tomaron datos físicos de los ejemplares, como tallas y peso. Mientras tanto, el equipo de investigación del Laboratorio de Ecología Molecular de la misma universidad extrajo los estómagos de las totoabas y los colocó en charolas de disección (Figura 4). Los estómagos fueron cuidadosamente abiertos para evitar contaminaciones y se encontraron partes de peces como anchovetas, así como estructuras duras como escamas y huesos. A pesar de la digestión avanzada, se lograron extraer seis muestras del contenido estomacal para analizarlas en el laboratorio.
¿Qué comieron las totoabas adultas?
Gracias al análisis metagenómico, se descubrió que las totoabas se alimentan de al menos 11 especies diferentes. Las presas más comunes fueron la anchoveta del Pacífico (Cetengraulis mysticetus), la lisa común (Mugil cephalus), la anchoveta de California (Engraulis mordax) y el chano norteño (Micropogonias megalops), todas ellas especies comunes en el Golfo de California. También se identificaron diversas especies de krill, pequeños crustáceos similares a camarones (Figura 5).
Figura 5. Principales especies consumidas por la totoaba.
Crédito: A. Abadía (2023).
Se encontraron parásitos y microorganismos en el contenido estomacal, pero estos no forman parte de su dieta, sino que probablemente fueron ingeridos incidentalmente (Mroue-Ruiz et al., 2023).
Este estudio es el primero en documentar la dieta de la totoaba mediante metagenómica, una técnica que ofrece muchas ventajas sobre los métodos tradicionales. Análisis previos basados en técnicas convencionales (Berdegué, 1955; De Anda-Montañez et al., 2013) sólo habían identificado cinco de las 11 especies encontradas en este estudio, lo que demuestra la mayor precisión de la metagenómica.
Si bien la metagenómica es una herramienta valiosa, no está exenta de limitaciones. Por ejemplo, sólo permite detectar la presencia o ausencia de una especie en la muestra, sin proporcionar información sobre la cantidad de presas consumidas, su tamaño, etapa de desarrollo o sexo. Por ello, se recomienda complementarla con técnicas tradicionales de reconocimiento morfológico en futuros estudios. De esta manera, se obtendrá un panorama más completo que incluya tanto la identificación de especies como la cantidad consumida de cada una.
¿Cómo ayuda la metagenómica en la conservación de la totoaba?
El uso de la metagenómica como método alternativo para analizar la dieta de la totoaba tiene implicaciones importantes para su conservación y el manejo de sus poblaciones en cautiverio. Este estudio permite comprender mejor la interacción de la totoaba con otras especies a través de su alimentación, así como analizar variaciones en su dieta a lo largo del año o entre individuos de diferentes edades.
Uno de los mayores desafíos en el cultivo de totoaba ha sido la formulación de dietas adecuadas para su óptimo desarrollo. Gracias a este estudio, ahora es posible diseñar dietas más cercanas a su alimentación natural, lo que podría mejorar la supervivencia, la salud y el crecimiento de los ejemplares criados en cautiverio.
En conclusión, este trabajo amplía el conocimiento sobre la dieta de la totoaba en su entorno natural y demuestra las ventajas de la metagenómica como herramienta para la investigación biológica y la conservación de esta especie emblemática.
El avance científico permite mejorar la precisión de las investigaciones y optimizar el manejo de los recursos naturales. Al aplicar herramientas innovadoras como la metagenómica, se promueve la conservación de especies clave y se favorece la producción de alimentos sanos y sostenibles, con un impacto positivo en la salud del planeta y en nuestra calidad de vida.
Agradecimientos
Agradecemos a la Dra. Asunción Lago Lestón y a la Biól. Fadya Hussein Mroue Ruiz por su participación fundamental en la realización de este proyecto. El proyecto fue financiado por la 20ª convocatoria interna de la Universidad Autónoma de Baja California. También agradecemos al personal de la Unidad de Manejo Ambiental (uma) de Reproducción y Crianza de Totoaba de la uabc por su apoyo en la facilitación de los especímenes.
Referencias
- Arvizu, J., y Chávez, H. (1972). Sinopsis sobre la biología de la totoaba, Cynoscion macdonaldi, Gilbert 1890. fao Fisheries Synopsis, 108, 26.
- Berdegué, A. J. (1955). La pesquería de totoaba (Cynoscion macdonaldi) en San Felipe, Baja California. Revista de la Sociedad Mexicana de Historia Natural, 16, 45–78.
- Cisneros-Mata, M. A., Montemayor-Lopez, G., y Roman-Rodriguez, M. J. (1995). Life history and conservation of Totoaba macdonaldi. Conservation Biology, 9(4), 806–814. https://www.jstor.org/stable/2386990.
- Cisneros-Mata, M. A., Román-Rodríguez, M. J., Rodríguez-Félix, D., y Castellanos-Rico, M. A. (2020). Captura ilegal de totoaba. In M. A. Cisneros-Mata (Ed.), *Evaluación de la población de Totoaba macdonaldi. Instituto Nacional de Pesca y Acuacultura.
- De Anda-Montañez, J. A., García de León, F. J., Zenteno-Savín, T., Balart-Paez, E., Méndez-Rodríguez, L. C., Bocanegra-Castillo, N., Martínez-Aguilar, S., Campos-Dávila, L., Román Rodríguez, M. J., Valenzuela-Quiñonez, F., Rodríguez-Jaramillo, M. E., Meza-Chávez, M. E., Ramírez-Rosas, J. J., Saldaña-Hernández, I. J., Olguín-Monroy, N. O., y Martínez-Delgado, M. E. (2013). Estado de salud y estatus de conservación de la(s) población(es) de totoaba (Totoaba macdonaldi) en el Golfo de California: Una especie en peligro de extinción. Centro de Investigaciones Biológicas del Noroeste, S. C. La Paz, Baja California. Informe Final.
- Enríquez Paredes, L. M. (2023). Evaluación del impacto y pertinencia de las liberaciones experimentales de totoaba (Totoaba mcdonaldi) producida en cautiverio como estrategia de conservación de la población silvestre. Universidad Autónoma de Baja California. Informe final SNIB-CONABIO.
- Fernandes, K., van der Heyde, M., Bunce, M., Dixon, K., Harris, R. J., Wardell-Johnson, G., y Nevill, P. G. (2018). DNA metabarcoding—a new approach to fauna monitoring in mine site restoration. Restoration Ecology, 26(6), 1098–1107. https://doi.org/10.1111/rec.12868.
- Mroue-Ruiz, F. H., Pacheco-Sandoval, A., Lago-Lestón, A., Giffard-Mena, I., Abadía-Cardoso, A., Chong-Robles, J., y Schramm, Y. (2023). Metabarcoding used for the first time to identify prey of wild Totoaba macdonaldi. Integrative and Comparative Biology, 63(2), 276–287. https://doi.org/10.1093/icb/icad030.
- Nielsen, J. M., Clare, E. L., Hayden, B., Brett, M. T., y Kratina, P. (2018). Diet tracing in ecology: Method comparison and selection. Methods in Ecology and Evolution, 9, 278–291. https://doi.org/10.1111/2041-210X.12869.
- Pompanon, F., Deagle, B. E., Symondson, W. O., Brown, D. S., Jarman, S. N., y Taberlet, P. (2012). Who is eating what: Diet assessment using next generation sequencing. Molecular Ecology, 21(8), 1931–1950.
- semarnat. (2010). Norma Oficial Mexicana NOM-059-SEMARNAT-2010. Publicada el 30 de diciembre de 2010 en el Diario Oficial de la Federación. Última reforma publicada el 14 de noviembre de 2019.
- Watson, J. D., y Crick, F. H. C. (1953). Molecular structure of nucleic acids: A structure for deoxyribose nucleic acid. Nature, 171, 737–738.
Recepción: 2023/10/12. Aceptación: 2024/10/04. Publicación: 2025/03/11.